Afsnit 8.5: Tosidet variansanalyse
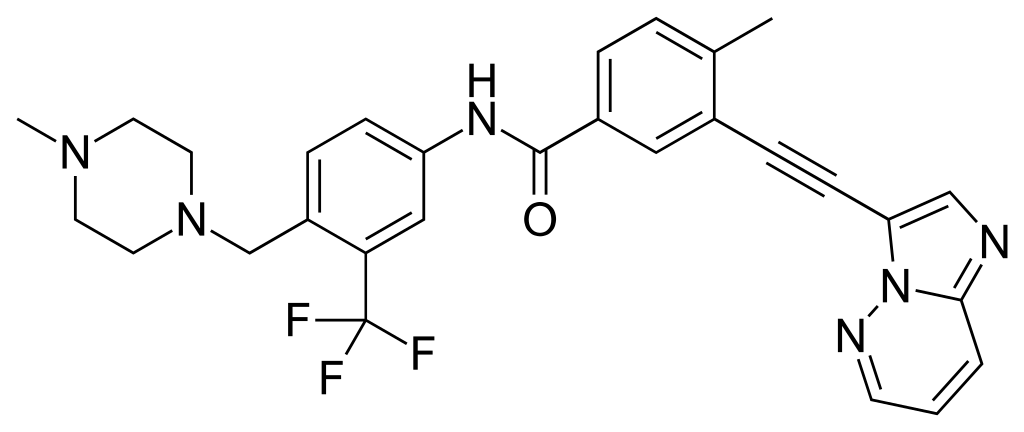
8.5.1 Boxplot opdelt efter to faktorer
Jeg vil nu beskrive den tosidede variansanalysemodel generelt. Data består af målinger fra uafhængige stokastiske variable Disse inddeles i grupper ved hjælp af to faktorer og Vi starter med en model, hvor både middelværdi og varians afhænger af, hvilken af de grupper observationen tilhører. For nemheds skyld betegnes niveauerne i de to faktorer blot med tal.Statistisk Model 8.5.2.
(Grundlæggende tofaktor gruppemodel)
Vi betragter uafhængige stokastiske variable
der deles ind i grupper efter en faktor med
faktorniveauerne og en faktor med
niveauerne Hver gruppe har sin egen middelværdi
og varians,
Når vi reducerer til modellen, hvor alle grupperne har den
samme varians, kaldes dette den tosidede variansanalysemodel. Statistisk Model 8.5.3.
(Tosidet variansanalysemodel (twoway anova))
Vi betragter uafhængige stokastiske variable
der deles ind i grupper efter en faktor med
faktorniveauerne og en faktor med
niveauerne Hver gruppe har sin egen middelværdi
og alle grupperne har samme varians,
Den tosidede variansanalysemodel har en meget vigtig undermodel
kaldet den additive model. Modellen er vigtig, da den giver
mulighed for simple fortolkninger af de parametre, der indgår,
hvilket beskrives detaljeret i næste afsnit. Statistisk Model 8.5.4.
(Additive model)
Vi betragter uafhængige stokastiske variable
der deles ind i grupper efter en faktor med
faktorniveauerne og en faktor med
niveauerne
Middelværdien i den additive model kan skrives som et bidrag fra
faktor
plus et bidrag fra faktor
Modellen har frie parametre i middelværdispecifikatioen.
Fra den additive model kan vi prøve at reducere modellen
til en model, hvor middelværdien kun har et bidrag fra
faktoren (eller kun har et bidrag fra faktoren ).
Dette fører os tilbage til den ensidede variansanalysemodel
8.2.3. For at få en fornemmelse af om data kan beskrives med den
additive model, kan man lave et interaktionsplot.
Den indbyggede funktion i python
er lidt mangelfuld på dette punkt,
så i stedet anbefaler jeg en funktion additivitetsPlot,
som findes i filen pytFunktioner.py. I et interaktionsplot beregner man gennemsnit i alle grupperne
givet ved opdeling efter Gennemsnit afsættes mod
niveauerne for den ene faktor, og alle gennemsnit, der ligger
på det samme niveau af den anden faktor, forbindes.
Hvis data kan beskrives med model ovenfor, afspejler
gennemsnittene i figuren altså afsat mod
for eksempel og punkterne
med samme værdi af forbindes. De kurver, der fremkommer,
svarer altså til kurven der parallelforskydes
med værdierne fra I et interaktionsplot prøver vi derfor
at vurdere, om kurverne ser ud til at være parallelle.
I det følgende kodevindue vises interaktionsplots baseret på
den indbyggede funktion interactionplot i
python.
Måden denne funktion kaldes på, fremgår af den følgende tabel.
De to variable inddel1 og inddel2 bruges til at dele
værdierne i variablen respons op i undergrupper.
Når I kører et program på jeres egen computer, kan I eventuelt
bruge den hjemmelavede funktion additivitetsPlot. Denne laver
en tilsvarende figur, men tilføjer også errorbars svarende til
plusminus standard error for gennemsnittet.
Funktionen ligger i filen pytFunktioner.py.
Begge figurer viser approksimative parallelle kurver, hvilket tyder på,
at data kan beskrives med den additive model.
ForegåendeNæste